近日,动物科技学院张勤教授团队在《Communications Biology》在线发表了题为“Improving multi-trait genomic prediction by incorporating local genetic correlations”的研究论文,该研究提出了三种整合局部遗传相关信息的多性状基因组预测方法用于提高基因组预测准确性。
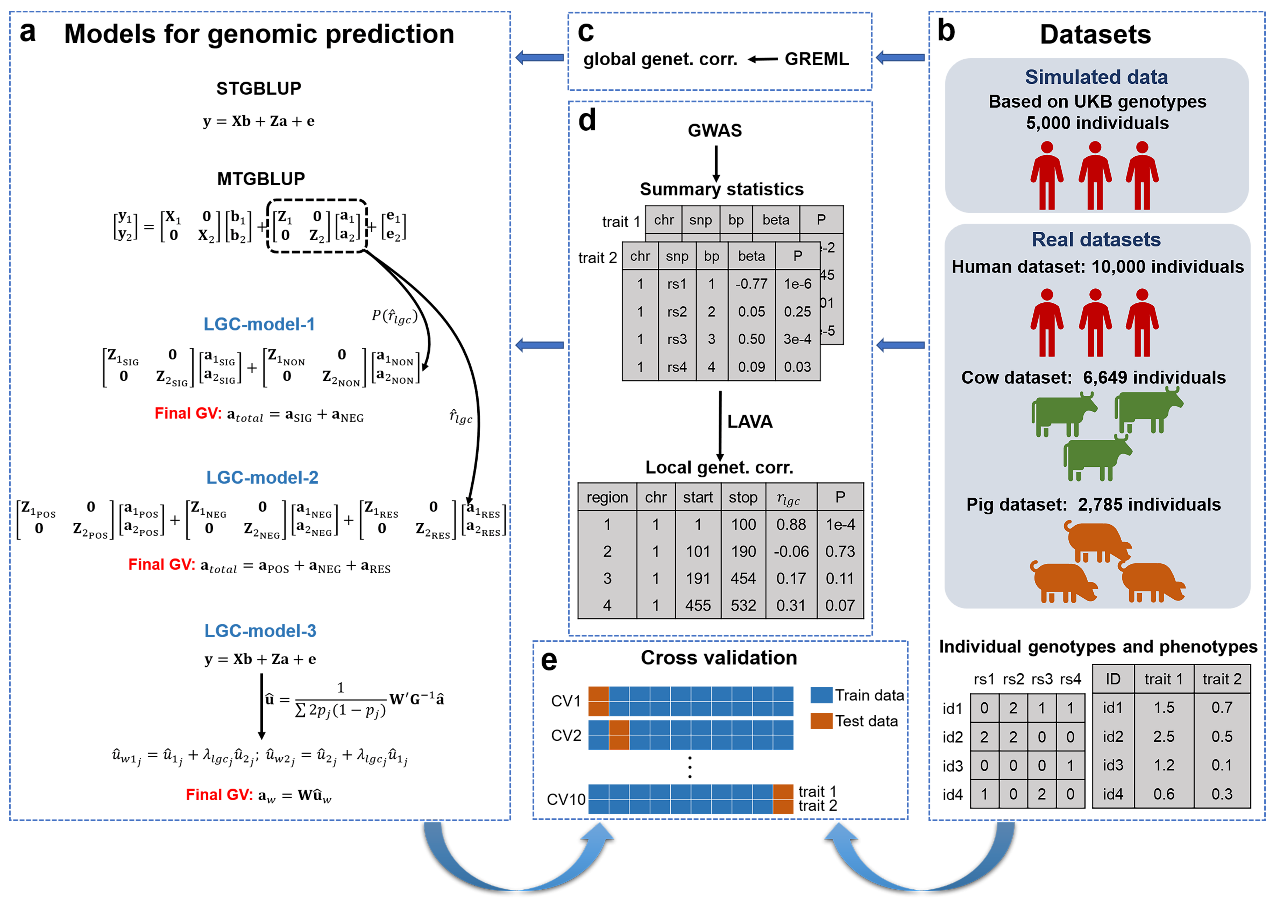
基因组预测在推动人类精准医疗以及加速动植物遗传改良方面具有巨大潜力。多性状基因组预测模型的预测准确性往往要优于单性状模型。然而,传统的多性状基因组预测模型(例如MTGBLUP)只考虑了性状间的整体遗传相关。随着局部遗传相关(LGC)估计方法的发展,现在可以分析特定基因组区域的性状间遗传相关,将局部遗传相关信息纳入多性状基因组预测模型有望提高预测准确性。我们提出了三种方法(LGC-model-1、LGC-model-2和LGC-model-3)来解决这一问题,并使用模拟数据和人类、牛和猪三个真实数据集评估了新方法的性能。研究结果表明,局部遗传相关在整个基因组中具有异质性。另外,与人类PRS模型(PRSice-2(C+T)、LDpred2和wMT-BLUP)和传统的多性状基因组预测模型(MTGBLUP)相比,三种方法可使预测准确性平均提高~12.76%。我们的研究结果凸显了考虑局部遗传相关信息对改进多性状基因组预测的重要性。
团队博士后滕军为该论文的第一作者,张勤教授和王丹教授为通讯作者。该研究得到国家重点研发计划、生物育种重大项目、扬州大学畜牧学学科特区学科交叉课题和山东省农业良种工程等项目的资助。
论文链接:https://doi.org/10.1038/s42003-025-07721-9
编 辑:万 千
审 核:贾 波









